Indice
Fresco, dissetante e protagonista indiscusso dell’estate, il cetriolo è ormai una presenza imprescindibile sui banchi dei mercati apprezzato dai consumatori per il suo apporto nutritivo e dai produttori per il valore economico. Tuttavia, la sua produzione deve spesso fare i conti con alcune avversità biotiche che interessano la coltura. Uno di questi è Corynespora cassiicola, il fungo responsabile del Target Leaf Spot (TLS), una malattia fungina in grado di compromettere resa e qualità del raccolto.
La Target Leaf Spot è ben nota in molte regioni tropicali e subtropicali, ma la sua ombra si è affacciata anche in Italia. La sua presenza è stata infatti documentata nel 2006 su basilico coltivato in serra in Liguria, come riportato dalla rivista Plant Disease. Sebbene da allora non siano emerse nuove segnalazioni ufficiali, il contesto agricolo attuale – segnato dagli effetti del cambiamento climatico che favorisce la diffusione di patogeni – rende indispensabile l’adozione di strategie preventive. In quest’ottica si inserisce uno studio condotto in Cina, dove un team di ricercatori è riuscito a individuare le regioni del DNA responsabili della resistenza del cetriolo, utilizzando strumenti all’avanguardia. Al centro dello studio c’è una tecnica moderna chiamata GWAS (Genome-Wide Association Study), che consente di analizzare il DNA di numerose piante per individuare i geni associati a caratteristiche specifiche, come appunto, la resistenza alle avversità.
Il cetriolo: come è stato condotto lo studio
Per condurre lo studio, i ricercatori hanno testato 130 varietà internazionali di cetriolo, rappresentative di quattro principali ecotipi: eurasiatico, indiano, est-asiatico e Xishuangbanna. Le piante sono state coltivate nella provincia di Shandong e sottoposte a infezione naturale da C. cassiicola in tre diverse stagioni, tra il 2021 e il 2023.
I sintomi della TLS sono comparsi intorno alla sesta settimana dalla semina e, per tre settimane consecutive, gli studiosi hanno monitorato attentamente lo stato di salute delle foglie, assegnando a ogni pianta un punteggio da 0 (nessuna lesione) a 9 (oltre il 75% della superficie fogliare colpita). Parallelamente, il fungo responsabile della malattia è stato coltivato in laboratorio e preparato in sospensione con una concentrazione definita di spore (100.000 per millilitro), così da assicurare un’infezione controllata. Il livello di malattia è stato poi calcolato con un indice specifico (DI), che ha considerato sia la frequenza sia la gravità dell’infezione.
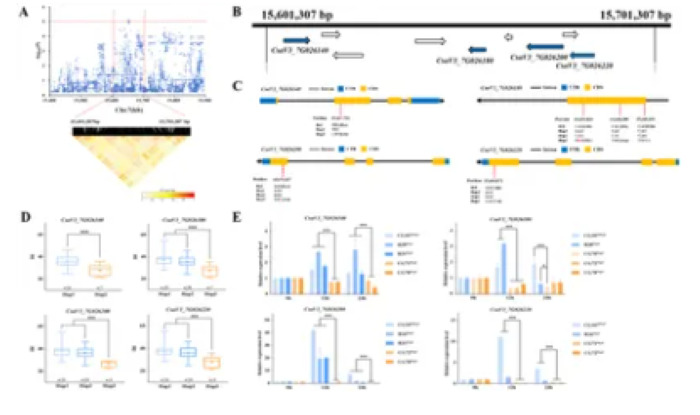
Analisi del gene candidato del locus gTLS7.1 . (A) Grafico Manhattan locale (sopra) e mappa di calore LD (sotto) che circonda il locus. La linea tratteggiata orizzontale rossa indica la soglia di significatività (-log 10 ( P ) > 5,1), e le linee tratteggiate rosse verticali indicano la regione candidata (100 kb). (B) Nove geni sono rappresentati con frecce che mostrano la loro polarità. Le frecce blu indicano i geni legati allo stress abiotico o alla resistenza alle malattie, con annotazioni dettagliate nella Tabella supplementare S6 . (C) Le strutture di CsaV3_7G026140 , CsaV3_7G026180 , CsaV3_7G026200 e CsaV3_7G026220 . I rettangoli blu e arancione rappresentano rispettivamente gli UTR e i CDS, e la linea orizzontale nera rappresenta gli introni. (D) Box plot che mostrano l’analisi dell’aplotipo di CsaV3_7G026140 con linee Hap1 e Hap2 , mentre mostrano l’analisi dell’aplotipo di CsaV3_7G026180 , CsaV3_7G026200 e CsaV3_7G026220 con genotipi Hap1 , Hap2 e Hap3 . I riquadri blu rappresentano il DI delle accessioni sensibili alla TLS che trasportano Hap1 (blu chiaro) e Hap2 (blu più scuro) . Il riquadro arancione rappresenta il DI delle accessioni resistenti alla TLS che trasportano Hap3 (*** p < 0,001). (E) Livello di espressione di CsaV3_7G026140 , CsaV3_7G026180 , CsaV3_7G026200 e CsaV3_7G026220 a 0, 12 e 24 ore dopo il trattamento di inoculazione. L’actina1 è stata utilizzata come controllo interno. I dati sono i valori medi con la deviazione standard (DS) di tre repliche biologiche indipendenti. Differenza significativa (*** p < 0,001, * p < 0,05). ns indica differenze non significative (p ≥ 0,05).
Dati precisi, geni identificati
A questo punto è entrata in gioco l’analisi GWAS, acronimo di Genome-Wide Association Study, una tecnica che ha permesso di sequenziare l’intero genoma di ciascuna varietà e identificare oltre 1,6 milioni di marcatori genetici (SNP) sparsi sui sette cromosomi del cetriolo. Grazie a questo, i ricercatori hanno identificato tre regioni del genoma fortemente associate alla resistenza alla TLS: due sul cromosoma 5 e una sul cromosoma 7. Una scoperta importante, che apre nuove strade rispetto a studi precedenti concentrati solo sul cromosoma 6.
Non solo: lo studio ha anche portato all’individuazione di cinque geni candidati, tra cui uno che codifica l’enzima ubiquitina ligasi E3, coinvolto sia nella risposta immunitaria che nella tolleranza allo stress salino. Altri geni sono legati alla struttura della parete cellulare o alla regolazione dell’equilibrio tra crescita e difesa: un aspetto cruciale per evitare che piante troppo “difensive” rallentino il loro sviluppo. Il risultato? Una mappa genetica dettagliata della resistenza alla TLS, utile per sviluppare nuove varietà di cetriolo più robuste e capaci di affrontare le sfide del cambiamento climatico e delle avversità.
Resistenti naturali: la forza dell’ecotipo Xishuangbanna
Tra le varietà studiate, l’ecotipo Xishuangbanna si è distinto per la sua resistenza non solo alla TLS, ma anche ad altre avversità comuni del cetriolo. Le 32 accessioni più resistenti appartenevano tutte a questo gruppo genetico, rendendolo un potenziale tesoro per i futuri programmi di breeding. Al contrario, le varietà eurasiatiche si sono rivelate le più vulnerabili. In definitiva, si tratta di uno studio che ha offerto informazioni preziose per comprendere più a fondo i meccanismi di resistenza alla TLS nei cetrioli. Un passo importante verso lo sviluppo di strategie di miglioramento genetico di precisione per coltivazioni più sane e sostenibili.
Federica Del Vecchio
©fruitjournal.com
